Replicación de ADN
El proceso de replicación, autorreplicación, duplicación o autoduplicación de ADN es el mecanismo que permite al ADN duplicarse (es decir, sintetizar una copia idéntica). De esta manera, de una molécula de ADN única, se obtienen dos o más "réplicas". Esta duplicación del material genético se produce de acuerdo con un mecanismo semiconservador, lo que indica que los dos polímeros complementarios del ADN original, al separarse, sirven de molde cada una para la síntesis de una nueva cadena complementaria de la cadena molde, de forma que cada nueva doble hélice contiene una de las cadenas del ADN original. Gracias a la complementación entre las bases que forman la secuencia de cada una de las cadenas, el ADN tiene la importante propiedad de reproducirse idénticamente, lo que permite que la información genética se transmita de una célula madre a las células hijas y es la base de la herencia del material genético.
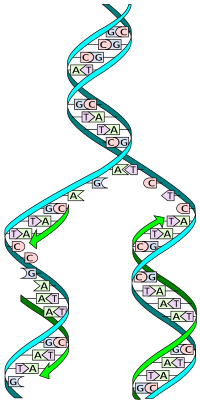
La molécula de ADN se abre como una cremallera, por ruptura de los puentes de hidrógeno entre las bases complementarias en puntos determinados: los orígenes de replicación. Las proteínas iniciadoras reconocen secuencias de nucleótidos específicas en esos puntos y facilitan la fijación de otras proteínas que permitirán la separación de las dos hebras de ADN formándose una horquilla de replicación. Un gran número de enzimas y proteínas intervienen en el mecanismo molecular de la replicación, formando el llamado complejo de replicación o replisoma. Estas proteínas y enzimas son homólogas en eucariotas y arqueas, pero difieren en bacterias.
Características generales del ADN
editar- Es una cadena molecular, quiere decir que es una sustancia constituida por distintos tipos de moléculas sencillas ligadas entre sí para así ir formando cadenas.
- Es bastante largo y extremadamente delgado. Si aumentáramos cien veces el tamaño del núcleo celular alcanzaría el tamaño de la punta de un alfiler, mientras que el ADN plegado en ese mismo núcleo alcanzaría la longitud de un campo de fútbol.
- Hay cuatro tipos de eslabones, esos son las moléculas denominadas nucleótidos en la cadena. Sus nombres son: ácido adenílico (adenina), ácido guanílico (guanina), ácido citidílico (citosina) y ácido timidílico (timina) y las abreviaturas, A, G, C, T, para cada una.
Semiconservadora
editarEn cada una de las moléculas hijas se conserva una de las cadenas originales, y por eso se dice que la replicación del ADN es semi conservadora. Hasta que finalmente se pudo demostrar que la replicación es semiconservadora, se consideraron tres posibles modelos para el mecanismo de la replicación:
- Semiconservadora (modelo correcto). En cada una de las moléculas hijas se conserva una de las cadenas originales.
- Conservadora. Se sintetiza una molécula totalmente nueva, copia de la original.
- Dispersora, o dispersante. Las cadenas hijas constan de fragmentos de la cadena antigua y fragmentos de la nueva.
El experimento de Meselson y Stahl en 1958 permitió demostrar que el mecanismo real se ajusta a la hipótesis de replicación semiconservadora. Para ello se hicieron crecer células de Escherichia coli en presencia de nitrógeno-15, un isótopo del nitrógeno más pesado de lo habitual. En consecuencia, el isótopo se incorporó a las cadenas de ADN que se iban sintetizando, haciéndolas más pesadas.
Una vez conseguido el primer objetivo, las células fueron transferidas a un medio que contenía nitrógeno-14, es decir, un medio más ligero, donde continuaron su crecimiento (división celular, que requiere la replicación del ADN). Se purificó el ADN y se analizó mediante una centrifugación en gradiente de cloruro de cesio, en donde hay más densidad en el fondo del tubo que en la parte media del mismo.
En la primera generación (figura 2.b) se obtuvo una única banda de ADN con densidad intermedia. En la segunda generación (figura 2.c) se obtuvieron dos bandas, una con densidad ligera y otra con densidad intermedia o híbrida. En la tercera generación se obtuvieron dos bandas, una ligera (con una abundancia del 75 %) y otra intermedia (con el 25 % restante).
La banda intermedia o híbrida representa una molécula de ADN que contiene una cadena pesada (original) y otra ligera (recién sintetizada). Las cadenas ligeras representan una molécula de ADN en la que las dos cadenas han sido sintetizadas (no existían aun cuando las células se pusieron en presencia de nitrógeno-15).
El hecho de que cada vez haya más moléculas ligeras y se mantenga el número de moléculas intermedias demuestra que la replicación del ADN es semiconservadora. Si fuera conservadora, aparecería siempre una banda pesada y el resto ligeras (figuras 1.a, 1.b, 1.c) . Si fuera dispersante solo aparecerían bandas híbridas de densidad intermedia en todas las generaciones.[1]
Secuencial y bidireccional desde puntos fijos
editarLos orígenes de replicación son los puntos fijos a partir de los cuales se lleva cabo la replicación, que avanza de forma secuencial formando estructuras con forma de horquilla. Por otro lado, la replicación se lleva a cabo bidireccionalmente, es decir, a partir de cada origen se sintetizan las dos cadenas en ambos sentidos.
El origen de replicación
editarLa cantidad de ADN que se puede sintetizar a partir de un único origen de replicación se denomina replicón o unidad funcional de replicación. El genoma bacteriano es un replicón único circular. En organismos eucarióticos, la replicación del ADN se inicia en múltiples orígenes a la vez (hay uno cada 20 kb aproximadamente), es decir, hay varios replicones.[2]
Los experimentos realizados por Cairns (1963) con bacterias Escherichia coli permitieron determinar la existencia de ese punto fijo u origen de replicación a partir del cual el genoma empezaba a replicarse. Los experimentos consistían en mantener un cultivo de E. coli creciendo en un medio que contenía timidina tritiada (timina marcada con tritio), de forma que el ADN quedara marcado radiactivamente pudiendo efectuarse una autorradiografía. A continuación se observaba al microscopio. Los resultados indicaban que la replicación en E. coli se iniciaba en un punto concreto (OriC).[3]
Secuencialidad
editarSueoka y Yoshikawa (1963) realizaron estudios genéticos de complementación de mutaciones que permitieron determinar que desde los orígenes la replicación avanza de forma secuencial. Trabajaron con Bacillus subtilis porque era posible obtener cultivos sincronizados de forma que todas las células del cultivo estuvieran en la misma fase del ciclo celular. El método consistía en la conjugación bacteriana de cepas silvestres con cepas mutantes incapaces de sintetizar determinados aminoácidos. Conociendo la localización de los genes que codifican las proteínas implicadas en la síntesis de los diferentes aminoácidos en el cromosoma bacteriano, y haciendo crecer las bacterias receptoras en un «medio mínimo» (donde solo pudiesen crecer las que hubieran recibido alguno de estos genes), al extraer ADN a diferentes tiempos se observó que, tras la última extracción aparecía con mayor frecuencia el gen implicado en la síntesis de uno de los aminoácidos (el correspondiente a la "posición 1"), que el gen adyacente implicado en la síntesis de otro aminoácido ("posición 2"). De la misma forma, el gen que ocupaba la "posición 3" aparecía con menor frecuencia que el que ocupaba la "posición 2", y así sucesivamente.
Como los primeros genes en replicarse en la bacteria donadora serían los primeros en transferirse, el experimento permitió demostrar, a partir de las frecuencias relativas de los diferentes genes en las bacterias receptoras, que la replicación sigue un orden (es secuencial).
La replicación avanza en forma de horquilla
editarDebido a que en la célula ambas cadenas de la doble hélice de ADN se duplican al mismo tiempo, éstas deben separarse para que cada una de ellas sirva de molde para la síntesis de una nueva cadena. Por eso, la replicación avanza con una estructura en forma de horquilla formándose una burbuja u ojo de replicación (también llamada estructura θ cuando el ADN es circular debido a la similitud entre la letra griega y la forma que adopta el cromosoma bacteriano en estados intermedios de replicación, no obstante pudiendo aparecer estructuras alternativas),[3] que avanza en dirección a la región de ADN no duplicado dejando atrás los dos moldes de ADN de cadena simple donde se está produciendo la replicación.[2]
Bidireccionalidad
editarEl movimiento de la horquilla es bidireccional en la mayoría de los casos, es decir, a partir de un punto se sintetizan las dos cadenas en ambos sentidos. Esto ocurre en la mayoría de los organismos, pero se dan excepciones en algunos procariontes debido a que los mecanismos de replicación que tienen lugar dependen de la propia estructura de su material hereditario (si el ADN es circular, lineal, bicatenario o monocatenario).[3] Así, en casos particulares como el ADN mitocondrial, algunos plásmidos y algunos genomas monocatenarios de fagos pequeños, la replicación se da unidireccionalmente pudiendo haber uno o dos orígenes de replicación.
No obstante, la replicación se puede considerar, de forma general, bidireccional.
La evidencia experimental del crecimiento bidireccional de la hebra de ADN viene dada por una técnica basada en el marcaje radiactivo del ADN usando timidina marcada con tritio. Primero se añade timidina sin marcar y luego marcada con tritio; siguiendo el rastro de tritio se observa hacia dónde se ha replicado la molécula de ADN.[3] También se puede, mediante el recuento de copias de genes marcadores, determinar si la replicación es unidireccional o bidireccional. Otras técnicas se basan en medir la distancia desde los ojos de replicación hasta los extremos de un ADN lineal (o circular convertido en lineal mediante enzimas de restricción).
Semidiscontinua
editarLa replicación siempre se produce en sentido 5' → 3', siendo el extremo 3'-OH libre el punto a partir del cual se produce la elongación del ADN. Esto plantea un problema, y es que las cadenas tienen que crecer simultáneamente a pesar de que son antiparalelas, es decir, que cada cadena tiene el extremo 5' enfrentado con el extremo 3' de la otra cadena. Por ello, una de las cadenas debería ser sintetizada en dirección 3' → 5'.
Este problema lo resolvieron los científicos japoneses Reiji Okazaki y Tsuneko Okazaki en la década de 1960, al descubrir que una de las nuevas cadenas de ADN se sintetiza en forma de trozos cortos que, en su honor, se denominan fragmentos de Okazaki. Su longitud suele variar entre 1000 y 2000 nucleótidos en las bacterias y entre 100 y 400 nucleótidos en eucariontes.
La cadena que se sintetiza en el mismo sentido que avanza la horquilla de replicación se denomina hebra adelantada o conductora y se sintetiza de forma continua por la ADN polimerasa, mientras que la que se sintetiza en sentido contrario al avance se denomina hebra rezagada o retrasada, cuya síntesis se realiza de forma discontinua teniendo que esperar a que la horquilla de replicación avance para disponer de una cierta longitud de ADN molde.[2]
ADN Polimerasas
editarEl ADN polimerasa es la enzima que cataliza la síntesis de la nueva cadena de ADN a partir de desoxirribonucleótidos y de la molécula de ADN plantilla o molde que es la que será replicada. La enzima copia la cadena de nucleótidos de forma complementaria (A por T, C por G) para dar a cada célula hija una copia del ADN durante la replicación.
Modo de operación
editarEn cada horquilla de replicación, el ADN polimerasa y otras enzimas sintetizan dos nuevas cadenas de ADN que son complementarias respecto a las dos cadenas originales. Durante este proceso, el ADN polimerasa reconoce una base nucleotídica no apareada de la cadena original y la combina con un nucleótido libre que tiene la base complementaria correcta. Luego, el ADN polimerasa cataliza la formación de nuevos enlaces covalentes que ligan el fosfato del nucleótido libre entrante con el azúcar del nucleótido previamente agregado en la cadena hija en crecimiento. De esta forma, el ADN polimerasa sintetiza el esqueleto de azúcar-fosfato de la cadena hija.
Los ADN polimerasas también realizan otras funciones durante el proceso de replicación. Además de participar en la elongación, desempeñan una función correctora y reparadora gracias a su actividad exonucleasa 3', que les confiere la capacidad de degradar el ADN partiendo de un extremo de este. Es importante que existan estos mecanismos de corrección ya que de lo contrario los errores producidos durante la copia del ADN darían lugar a mutaciones.
Proceso general
editar- La topoisomerasa relaja la tensión provocada por el superenrollamiento del ADN al abrirse las dos hebras
- La helicasa rompe los puentes de hidrógeno de la doble hélice, abriendo las dos hebras, permitiendo el avance de la horquilla de replicación.
- Las proteínas SSB estabilizan las cadenas abiertas y las mantienen separadas una de otra.
- El cebador fragmentos de ARN que se unen a la cadena molde por puentes de hidrógeno para que el ADN polimerasa III reconozca donde debe unirse para empezar a añadir nucleótidos.
- El ADN polimerasa I reemplaza los cebadores de ARN por nucleótidos de ADN.
- El ADN polimerasa II interviene en la corrección de errores.
- El ADN polimerasa III sintetiza la cadena complementaria de forma continua en la hebra adelantada y de forma discontinua en la hebra rezagada, ya que solo puede sintetizar en dirección 5'→ 3'.
- El ARN primasa sintetiza el cebador de ARN necesario para la síntesis de la cadena complementaria a la cadena rezagada.
- El ADN ligasa une los fragmentos de Okazaki.
El proceso se puede dividir en 3 fases: iniciación, elongación y terminación.
Iniciación
editarMediante consumo de ATP en dirección a la horquilla de replicación, es decir, en dirección 3' → 5' en la hebra rezagada y 5' → 3' en la hebra adelantada, la helicasa actúa rompiendo los puentes de hidrógeno que mantienen unida la doble hélice.[3] El siguiente conjunto de proteínas reclutadas son las denominadas proteínas SSB[nota 1] encargadas de la estabilización del ADN monocatenario generado por la acción de las helicasas, impidiendo así que el ADN se renaturalice o forme de nuevo la doble hélice, de manera que pueda servir de molde. Estas proteínas se unen de forma cooperativa, por lo que su unión al ADN conforme avanza la helicasa es rápida. Por otro lado, conforme las helicasas van avanzando se van generando superenrollamientos en la doble cadena de ADN por delante de la horquilla y si éstos no fueran eliminados, llegado a un punto el replisoma ya no podría seguir avanzando. Las topoisomerasas son las enzimas encargadas de eliminar los superenrollamientos cortando una o las dos cadenas de ADN y pasándolas a través de la rotura realizada.[2]
Elongación
editarEn el siguiente paso, el ADN Pol III cataliza la síntesis de las nuevas cadenas añadiendo nucleótidos sobre el molde. Esta síntesis se da bidireccionalmente desde cada origen, con dos horquillas de replicación que avanzan en sentido opuesto. Cuando el avance de dos horquillas adyacentes las lleva a encontrarse, es decir, cuando dos burbujas se tocan, se fusionan, y cuando todas se han fusionado todo el cromosoma ha quedado replicado.
Puesto que el ADN Pol III necesita de un extremo 3'-OH libre, es necesario que un ARN primasa catalice la formación de un fragmento corto específico de ARN llamado cebador, que determinará el punto por donde la ADN polimerasa comienza a añadir nucleótidos. Así, durante la síntesis, en cada horquilla de replicación se van formando dos copias nuevas a partir del cebador sintetizado en cada una de las dos hebras de ADN que se separaron en la fase de iniciación, pero debido a la unidireccionalidad de la actividad polimerasa de la ADN Pol III, que solo es capaz de sintetizar en sentido 5´ → 3', la replicación solo puede ser continua en la hebra adelantada; en la hebra rezagada es discontinua, dando lugar a los fragmentos de Okazaki.
La mitad del dímero del ADN Pol III sintetiza la hebra adelantada y la otra mitad la hebra rezagada.[3] La elongación de la hebra rezagada ocurre por medio del modelo del trombón.
En la hebra rezagada, cuando el ADN Pol III hace contacto con el extremo de otro fragmento de Okazaki contiguo, el cebador de ARN de este es eliminado y los dos fragmentos de Okazaki de ADN recién sintetizado son unidos. Una vez se han juntado todos se completa la doble hélice de ADN. La eliminación de cebadores también se da en la hebra conductora, de síntesis continua, pero debido a que en ésta hay un solo cebador es un proceso que solo tiene lugar una vez, mientras que en la hebra rezagada se dará tantas veces como fragmentos de Okazaki haya.
En la eliminación del cebador (también denominado iniciador o partidor) intervienen dos enzimas: por un lado el ADN Pol I, que va eliminando el ARN con su actividad exonucleasa 3' → 5' y simultáneamente rellenando con ADN mediante su actividad polimerasa 5' → 3' (proceso denominado nick-traslation). Al final queda rotura (o «mella») entre el extremo 3'-OH libre y el fosfato 5' de la cadena sintetizada; por último, el ADN ligasa sella esa rotura catalizando la reacción de condensación entre el grupo fosfato y el OH de la desoxirribosa del nucleótido contiguo, completando el enlace fosfodiéster; para ello, es preciso hidrolizar una molécula de ATP.[2]
Nota: diversos autores difieren en las enzimas implicadas en esta etapa. Para algunos no es el propio ADN Pol I la que rellena el hueco tras eliminar el cebador, sino que lo hace el ADN Pol III (la misma que polimeriza el resto de la cadena). Del mismo modo, algunos autores siguen empleando el término ribonucleasa o (ARNasa) para referirse al ADN Pol I en esta etapa, ya que hasta hace poco se desconocía que la propia ADN Pol I tenía la capacidad exonucleasa 3' → 5', y se pensaba que esto lo realizaba otro enzima, que recibía este nombre genérico.
Terminación (de los genomas lineales)
editarEl final de la replicación se produce cuando al ADN polimerasa III se encuentra con una secuencia de terminación. Se produce entonces el desacople de todo el replisoma y la finalización de la replicación.
Véase también
editarNotas
editar- ↑ Proteínas SSB siglas de su nombre en inglés single-stranded DNA binding proteins, proteínas ligantes de ADN monocatenario
Referencias
editar- ↑ Watson, J. D.; Baker, T. A.; Bell, S. P.; Gann, A.; Levine, M. et Losick, R (2006). «2. Los ácidos nucleicos transmiten información genética». Biología Molecular del Gen (5.ª ed.). Madrid: Médica Panamericana. 84-7903-505-6.
- ↑ a b c d e Watson, J. D.; Baker, T. A.; Bell, S. P.; Gann, A.; Levine, M. et Losick, R (2006). «8. La duplicación del DNA». Biología Molecular del Gen (5ª Ed.). Madrid: Médica Panamericana. 84-7903-505-6.
- ↑ a b c d e f César Benito Jiménez, Profesor Titular de Genética, Departamento de Genética, U.C.M. «La Replicación». Consultado el marzo de 2008.
Bibliografía
editar- Bramhill, D., and Kornberg, A. 1988. A model for initiation at origins of DNA replication. Cell 54:915-18.
Enlaces externos
editar- Replicación del ADN con audio en español.
- Visualización molecular del ADN: Replicación de ADN.
- Animación sobre la replicación en E. coli.
- Animación interactiva sobre la replicación del ADN.
- Animación interactiva: enzimas que participan en la replicación del ADN.
- Varias animaciones de la replicación.