Virus ARN
Un virus ARN es un virus que usa ácido ribonucleico (ARN) como material genético, o bien que en su proceso de replicación necesita el ARN. Por ejemplo, el virus de la hepatitis B es un virus clasificado como virus ADN (hepadnavirus), con la peculiaridad de tener su genoma ADN de doble cadena y el genoma es transcrito en ARN durante la replicación.[1] Su ácido nucleico es usualmente ARN monocatenario, pero también puede ser ARN bicatenario. Los virus ARN monocatenarios pueden clasificarse, a su vez, según el sentido o polaridad de su ARN en negativos o positivos. Los virus ARN positivos son idénticos al ARNm viral y por lo tanto pueden ser inmediatamente traducidos por la célula huésped. El ARN viral negativo es complementario del ARNm y por lo tanto debe convertirse en ARN positivo por una ARN polimerasa antes de la traducción.[2]
Los retrovirus, al contrario que otros virus ARN monocatenarios, usan ADN intermedio para replicarse. En la transcriptasa inversa, una enzima viral procedente del propio virus, convierte el ARN viral en una cadena complementaria de ADN, que se copia para producir una molécula de ADN bicatenario viral. Este ADN dirige la formación de nuevos viriones.
Los virus ARN presentan generalmente tasas de mutación muy altas pues carecen de ADN polimerasas que puedan detectar y corregir los errores (reparación del ADN). Los virus ADN presentan tasas de mutación mucho más bajas debido a la habilidad de corrección de las ADN polimerasas de la célula huésped. Los retrovirus integran un ADN intermediario de su genoma ARN en el genoma del huésped, y por lo tanto tienen una oportunidad mayor de corregir errores en su genoma gracias a la acción de corrección de las ADN polimerasas de la célula huésped.
Aunque usualmente el ARN muta rápidamente, un reciente trabajo de investigación determinó que el virus del SARS y otros virus relacionados contienen un gen que muta muy lentamente.[3] El gen en cuestión tiene una estructura tridimensional compleja que se supone proporciona una función química necesaria para la propagación del virus, quizás como una ribozima. Si esto fuese así, la mayoría de las mutaciones la harían inútil para este fin y no se propagarían.
Clasificación de Baltimore y replicación editar
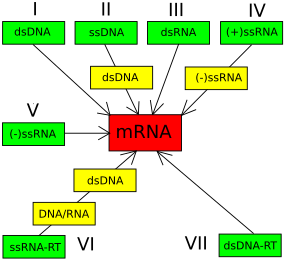
Los virus de ARN tienen genomas compuestos de ácido ribonucleico (ARN) y comprenden cuatro grupos: Grupo III: virus ARN bicatenario, Grupo IV: virus ARN monocatenario positivo, Grupo V: virus ARN monocatenario negativo y Grupo VI: virus ARN monocatenario retrotranscrito.
Virus ARN bicatenario editar
El tercer grupo de Baltimore contiene virus que tienen un genoma de ARN bicatenario. Después de entrar en una célula huésped, el genoma de ARN bicatenario se transcribe a ARNm de la hebra negativa por la ARN polimerasa dependiente de ARN (RdRp). El ARNm puede usarse para traducción o replicación. El ARNm monocatenario se replica para formar el genoma del dsRNA. El extremo 5' del genoma puede estar desnudo, protegido o unido covalentemente a una proteína viral.
El ARN bicatenario no es una molécula producida por las células, por lo que la vida celular ha desarrollado sistemas antivirales para detectar e inactivar el ARN bicatenario viral. Para contrarrestar esto, muchos genomas de ARN bicatenario se construyen dentro de las cápsides, evitando así la detección dentro del citoplasma de la célula huésped. El ARNm se expulsa de la cápside para ser traducido o translocado de una cápside madura a una cápside de progenie.
Virus ARN monocatenario positivo editar
El cuarto grupo de Baltimore contiene virus que tienen un genoma de ARN monocatenario positivo. Para los virus ARN monocatenario positivo, el genoma funciona como ARNm, por lo que no se requiere transcripción para la traducción. Sin embargo, los virus de ARN monocatenario positivo también producirán copias de sentido positivo del genoma a partir de cadenas de sentido negativo de un genoma de ARN monocatenario positivo intermedio. Esto actúa tanto como un proceso de transcripción como de replicación, ya que el ARN replicado también es ARNm. El extremo 5' puede estar desnudo, protegido o unido covalentemente a una proteína viral, y el extremo 3' puede estar desnudo o poliadenilado.
Muchos virus de ARN monocatenario positivo pueden tener solo una parte de su genoma transcrito. Normalmente, las hebras de ARN subgenómico (ARNsg) se utilizan para la traducción de proteínas estructurales y de movimiento necesarias durante las etapas intermedias y tardías de la infección. La transcripción de ARNsg puede ocurrir al comenzar la síntesis de ARN dentro del genoma en lugar del extremo 5', al detener la síntesis de ARN en secuencias específicas en el genoma o, como parte de ambos métodos anteriores, sintetizar secuencias líder del ARN viral que luego se unen a cadenas de ARNsg. Debido a que la replicación es necesaria para la síntesis de ARNsg, RdRp siempre se traduce primero.
Debido a que el proceso de replicación del genoma viral produce moléculas de ARN bicatenario intermedias, los virus + ssRNA pueden ser atacados por el sistema inmunológico de la célula huésped. Para evitar la detección, los virus de ARN monocatenario positivo se replican en vesículas asociadas a la membrana que se utilizan como fábricas de replicación. A partir de ahí, solo el ARNm viral +, que puede ser ARNm, ingresa al área citoplásmica principal de la célula.
+ Los virus de ARN monocatenario positivo se pueden subdividir entre los que tienen ARNm policistrónico, que codifica una poliproteína que se escinde para formar múltiples proteínas maduras, y los que producen ARNm subgenómicos y, por tanto, se someten a dos o más rondas de traducción.
Virus ARN monocatenario negativo editar
El quinto grupo de Baltimore contiene virus que tienen un genoma de ARN monocatenario negativo. El ARNm, que es de sentido positivo, se transcribe directamente del genoma de sentido negativo. El primer proceso para la transcripción de ARN monocatenario negativo implica la unión de la RdRP a una secuencia líder en el extremo 3' del genoma, transcribiendo un ARN líder de trifosfato 5' que está protegido, luego se detiene y reinicia en una señal de transcripción que está bloqueada, continuando hasta se alcanza la señal de parada. La segunda forma es similar, pero en lugar de sintetizar una tapa, RdRp puede hacer uso de cap snatching, mediante el cual se toma una secuencia corta de ARNm de la célula huésped y se usa como la tapa 5' del ARNm viral. El ARN monocatenario negativo genómico se replica a partir del antigenoma de sentido positivo de una manera similar a la transcripción, excepto a la inversa, utilizando el antigenoma como molde para el genoma. La RdRp se mueve desde el extremo 3' al extremo 5' del antigenoma e ignora todas las señales de transcripción cuando sintetiza ARN monocatenario negativo genómico.
Varios virus de ARN monocatenario negativo utilizan mecanismos especiales para la transcripción. La forma de producir la cola de poliA puede ser mediante la tartamudez de la polimerasa, durante la cual RdRp transcribe una adenina del uracilo y luego retrocede en la secuencia de ARN con el ARNm para transcribirlo nuevamente, continuando este proceso varias veces hasta que se hayan agregado cientos de adeninas al extremo 3' del ARNm. Además, algunos virus de ARN monocatenario negativo son ambisentidos, ya que las hebras positivas y negativas codifican proteínas virales por separado, y estos virus producen dos hebras de ARNm separadas: una directamente del genoma y otra de una hebra complementaria.
Los virus de ARN monocatenario negativo se pueden subdividir informalmente entre los que tienen genomas segmentados y no segmentados. Los virus de ARN monocatenario negativo no segmentados se replican en el citoplasma y los virus ARN monocatenario negativo segmentados se replican en el núcleo. Durante la transcripción, la RdRp produce una hebra de ARNm monocistrónico de cada segmento del genoma.
Virus ARN monocatenario retrotranscrito editar
El sexto grupo de Baltimore contiene virus que tienen un genoma de ARN monocatenario retrotranscrito (de sentido positivo) que tiene un ADN intermedio durante su ciclo de replicación. Los virus ARN monocatenario retrotranscrito se transcriben de la misma manera que los virus de ADN, pero sus genomas lineales primero se convierten en una forma de ADN bicatenario mediante un proceso llamado transcripción inversa. La enzima transcriptasa inversa viral sintetiza una hebra de ADN a partir de la hebra de ARN monocatenario retrotranscrito, y la hebra de ARN se degrada y se reemplaza por una hebra de ADN para crear un genoma de ADN bicatenario. Luego, el genoma se integra en el ADN de la célula huésped, donde ahora se denomina provirus. La ARN polimerasa II de la célula huésped luego transcribe el ARN en el núcleo del ADN provírico. Parte de este ARN puede convertirse en ARNm, mientras que otras cadenas se convertirán en copias del genoma viral para su replicación.
Mutación editar
Los virus de ARN experimentan una alta tasa de mutaciones genéticas que varían de a porque las polimerasas ARN polimerasa dependiente de ARN o transcriptasa inversa que portan son propensas a cometer errores en la replicación, ya que generalmente estos virus no usan ADN polimerasas para reparar los errores, salvo los virus de ARN retrotranscrito. Los virus de ARN son el segundo grupo biológico que muta más rápidamente, solo después de los viroides y virusoides que mutan diez más rápido que los virus de ARN con una tasa de , pues estos últimos se replican a través de ribozimas y no usan polimerasas. Las mutaciones en los virus de ARN a menudo están influenciadas por factores del hospedero, como las adenosina desaminasas dependientes de ARNdc, que editan los genomas virales cambiando las adenosinas por inosinas. Las mutaciones en genes que son esenciales para la replicación conducen a un número reducido de progenie, por lo que los genomas virales generalmente contienen secuencias que están altamente conservadas con el tiempo con relativamente pocas mutaciones.
Muchos virus de ARN experimentan una alta tasa severa de recombinación genética, aunque las tasas de recombinación varían significativamente, con tasas más bajas en los virus ARN monocatenario negativo y virus ARN monocatenario retrotranscrito, en cambio son mayores en los virus ARN bicatenario y ARN monocatenario positivo. Hay dos tipos de recombinación: recombinación por elección de copia y reordenamiento. La recombinación con opción de copia se produce cuando la polimerasa cambia las plantillas durante la síntesis sin liberar la cadena de ARN recién creada anterior, que genera un genoma de ascendencia mixta. El reordenamiento, que está restringido a virus con genomas segmentados, tiene segmentos de diferentes genomas empaquetados en un solo virión, o partícula de virus, que también produce una progenie híbrida.
Para el reordenamiento, algunos virus de ARN segmentados empaquetan sus genomas en múltiples viriones, lo que produce genomas que son mezclas aleatorias de padres, mientras que para aquellos que están empaquetados en un solo virión, típicamente se intercambian segmentos individuales. Ambas formas de recombinación solo pueden ocurrir si más de un virus está presente en una célula, y cuantos más alelos estén presentes, es más probable que ocurra la recombinación. Una diferencia clave entre la recombinación de elección de copia y el reordenamiento es que la recombinación de elección de copia puede ocurrir en cualquier parte de un genoma, mientras que el reordenamiento intercambia segmentos completamente replicados. Por lo tanto, la recombinación por elección de copia puede producir proteínas virales no funcionales, mientras que el reordenamiento no puede.
La tasa de mutación de un virus está asociada con la tasa de recombinaciones genéticas. Las tasas de mutación más altas aumentan tanto el número de mutaciones ventajosas como las desventajosas, mientras que las tasas de recombinación más altas permiten separar las mutaciones beneficiosas de las nocivas. Por lo tanto, las tasas más altas de mutaciones y recombinaciones, hasta cierto punto, mejoran la capacidad de adaptación de los virus. Ejemplos notables de esto incluyen reordenamientos que permiten la transmisión entre especies de influenzavirus o coronavirus, que han dado lugar a numerosas pandemias, así como la aparición de cepas resistentes a los medicamentos a través de mutaciones que se reagruparon.
Origen y evolución editar
El Comité Internacional de Taxonomía de Virus (ICTV) clasifica a todos los virus de ARN y los retrotranscritos, incluyendo los virus ADN bicatenario retrotranscrito en el dominio Riboviria, ya que estos se caracterizan por tener una ARN polimerasa dependiente de ARN (RdRP) o una transcriptasa inversa consideradas las polimerasas más primitivas existentes. Se divide en dos reinos Orthornavirae que incluye la mayoría de los virus de ARN, salvo algunos poco investigados y Pararnavirae que incluye los virus retrotranscritos, incluyendo los de ADN.
Se ha sugerido que los virus de ARN descienden de replicones de ARN primordiales que codificaban una ARN polimerasa dependiente de ARN (RdRP), anteriores al último antepasado común universal (LUCA) y que los eucariovirus de ARN descienden de virus de ARN procariotas en diferentes linajes. Los virus de ARN tienen una gran importancia evolutiva, ya que se ha sugerido que junto con los virusoides (Ribozyviria) y viroides son reliquias del antiguo mundo de ARN, puesto que su replicación se basa únicamente en el ARN (sin pasar por un extremo o secuencia de ADN, una característica ausente en las células) y que sus precedieron a los retroelementos de la vida celular (intrones y retrotransposones). El ancestro de los virus de ARN probablemente fue un replicón precelular de ARN similar a los mitovirus o endornavirus (sin capside) que codificaba una RdRP. Este replicón al fusionarse con la RdRP y proteínas de dominio palma, TNF, Pro-PD, CBM, nucleoplasminas y una JRC-MCP horizontal llevó a la formación de los viriones de los virus de ARN. De acuerdo con estudios recientes el filo basal de los virus de ARN es Taraviricota descubierto por metagenómica los cuales serían similares a los mitovirus o endornavirus (sin cápsides) y que infectarían a procariotas con pared celular deficiente y mitocondrias eucariotas. También se ha sugerido que los retroelementos de la vida celular intrones y retrotransposones se derivarían de un antepasado compartido con el filo Lenarviricota. Según estos estudios los tipos de genomas en los virus de ARN se fueron cambiando independientemente, aunque es probable que los primeros hayan sido de ARN monocatenario positivo.[4] Los virus de ARN eucarióticos pudieron llegar a estos por medio de las proteobacterias y las arqueas en el momento que sucedió la endosimbiosis seriada que involucró a una arquea y una proteobacteria las cuales darían origen a los eucariotas hace más de 2500 millones de años. Estos virus tuvieron una gran diversificación que representan una parte importante del viroma eucariota.[5]
Según el ICTV y otros estudios los virus de ARN se dividirían en los siguientes filos:[4]
- Reino Orthornavirae
- Filo Lenarviricota (ARN monocatenario positivo)
- Filo Duplornaviricota (ARN bicatenario)
- Filo Pisuviricota (ARN monocatenario positivo y ARN bicatenario)
- Filo Negarnaviricota (ARN monocatenario negativo)
- Filo Kitrinoviricota (ARN monocatenario positivo)
- Filo Artimaviricota (ARN bicatenario)
- Filo Taraviricota (ARN monocatenario positivo y ARN bicatenario)
- Filo Arctoviricota (ARN monocatenario negativo)
- Filo Paraxenoviricota (ARN monocatenario positivo)
- Filo Pomiviricota (ARN monocatenario positivo)
- Filo Wamoviricota (ARN monocatenario positivo)
Se ha sugerido que el filo Duplornaviricota debe ser dividido en tres filos separados. Los filos Taraviricota, Arctoviricota, Pomiviricota, Paraxenoviricota y Wamoviricota fueron descubiertos mediante muestras metagenómicas en los océanos y probablemente solo infecten microorganismos marinos.[4] El filo Artimaviricota fue descubierto en aguas termales ácidas e infectan bacterias termoacidofilas.[6]
Referencias editar
- ↑ a b N.J. Dimmock, A.J. Easton y K. Leppard, Introduction to Modern Virology, Ed. Wiley, 2006, ISBN 978-1-4051-3645-7
- ↑ Robertson MP, Igel H, Baertsch R, Haussler D, Ares M Jr, Scott WG (2005). «The structure of a rigorously conserved RNA element within the SARS virus genome». PLoS Biol 3 (1): e5. PMID 15630477 doi 10.1371/journal.pbio.0030005.
- ↑ a b c Cryptic and abundant marine viruses at the evolutionary origins of Earth’s RNA virome. Science org.
- ↑ Eugene V. Koonin, Mart Krupovic, and Vadim I. Agol, 2021. The Baltimore Classification of Viruses 50 Years Later: How Does It Stand in the Light of Virus Evolution?. American Society of Microbiogy.
- ↑ Double-stranded RNA sequencing reveals distinct riboviruses associated with thermoacidophilic bacteria from hot springs in Japan.